Master Bioinformatique
Diaporama de la réunion de pré-rentrée 29/08/2025
Diaporama de présentation de l’association ÉBiM
Présentation de MBI : Réseau montpelliérain en Bioinformatique
Présentation et objectifs
La formation en bioinformatique de l’Université de Montpellier a fêté ses 20 ans en 2021.
Anciennement parcours « Bioinformatique, Connaissance, Données » du master Sciences et Numérique pour la Santé, la formation bioinformatique est devenue le master Bioinformatique à la rentrée 2021.
Forte d’une équipe pédagogique pluridisciplinaire et d’un solide réseau d’entreprises et de laboratoires accueillant régulièrement ses stagiaires, elle propose aux étudiant·es venant de licences orientées informatique, mathématiques, biologie ou bioinformatique d’acquérir des connaissances de niveau master liées à la bioinformatique.
Le master Bioinformatique apporte une véritable double compétence et des savoir-faire propres à la Bioinformatique, ainsi qu’une connaissance théorique et pratique des domaines de la biologie et de l’informatique.
Les scientifiques pluridisciplinaires ainsi formé·es auront des compétences approfondies en :
- Analyse de données issues du vivant (statistiques, traitements algorithmiques, fouille de données) que ce soit au niveau des séquences, des données -omiques, des structures moléculaires, des données d’expression, etc.
- Conception de méthodes, d’outils, de bases et banques de données, et de systèmes d’information pour traiter ce type de données,
- Programmation dans différents environnements informatiques en adéquation avec le contexte biologique, passant par l’analyse des besoins, la conception de solutions et l’adaptation aux contraintes spécifiques,
- Diffusion et présentation des résultats des analyses.
Responsable de la formation

Annie Chateau, enseignante-chercheuse au département informatique.
Conditions d’accès
Être titulaire d’une Licence d’informatique, de mathématiques, de biologie ou de bioinformatique, ou d’un diplôme équivalent. Le master peut aussi se faire en formation continue et par apprentissage
Descriptif des enseignements
Débouchés de la formation
Les étudiant·es pourront exercer des métiers d’ingénieurs ou chercheurs dans les secteurs public et privé.
Dans le secteur privé, ils·elles pourront travailler dans une équipe R&D, que ce soit dans de grands groupes ou dans des PME innovantes. Alternativement, ils·elles pourront occuper des postes de cadre et à terme de chef de projet dans des Entreprises de Services du Numérique (ESN) pour la production d’outils logiciels dédiés.
Dans le secteur public, les professionnel·les formé·es seront en mesure d’occuper des emplois d’ingénieur hospitalier, d’ingénieur en bioinformatique permettant ainsi l’interface entre l’informatique et les sciences du vivant.
Un Master bien entouré
La formation est adossée à des équipes de recherche en informatique et en biologie (LIRMM,ISEM, IRMB, IGH, …) ce qui favorise les échanges entre les chercheur·es et les étudiant·es.
Enfin, la formation dispose d’une association d’étudiant·es (EBiM) et d’un réseau d’ancien·nes étudiant·es très actif.

Innovations pédagogiques
Chaque année depuis 2013, les étudiants de la formation organisent les Montpellier Omics Days (https://www.montpellier-omics-days.fr/), une manifestation scientifique autour des « Omiques » (génomique, transcriptomique, …) qui rassemble plus de 200 personnes à travers des conférences et des formations.

Depuis 2018, Anna-Sophie Fiston-Lavier, membre de l’équipe pédagogique du master de Bioinformatique, en collaboration avec des chercheurs et enseignants-chercheurs d’autres départements (Master IMHE) et composantes (IUT-Montpellier), animent un projet d’innovation pédagogique : le BioInformatics Learning Lab (BILL). Ce projet vise à simuler un laboratoire de recherche dans lequel les étudiants de différents parcours travaillent de manière collaborative sur un vrai projet de recherche de la collection de données jusqu’à la valorisation des résultats sous la forme de poster ou d’articles.

Alumni
- Amouzou Komlavi
- Beraud Lucas
- Bouvier Quentin
- Cafier Maxence
- Dahmani Noureddine
- Gomes Michel
- Heredia Carla
- Zellagui Miss Leriem
Imbert Jacques - Kamel Yascim
- Kon-Sun-Tack Fabien
- Marco Corentin
- Mille Marie
- Riedel Cédric
- Saab Nassif
- Sika Dassou
- Soulier Arnaud
- Soulier Arnaud
- Srihi Haythem
- Thimbo Seydi
- Toure Hadiaratou Ibrahim
- Zellagui Miss Leriem
Des doctorant·es en bioinfo (dont d’anciennes étudiantes du master) témoignent……

Pierre :
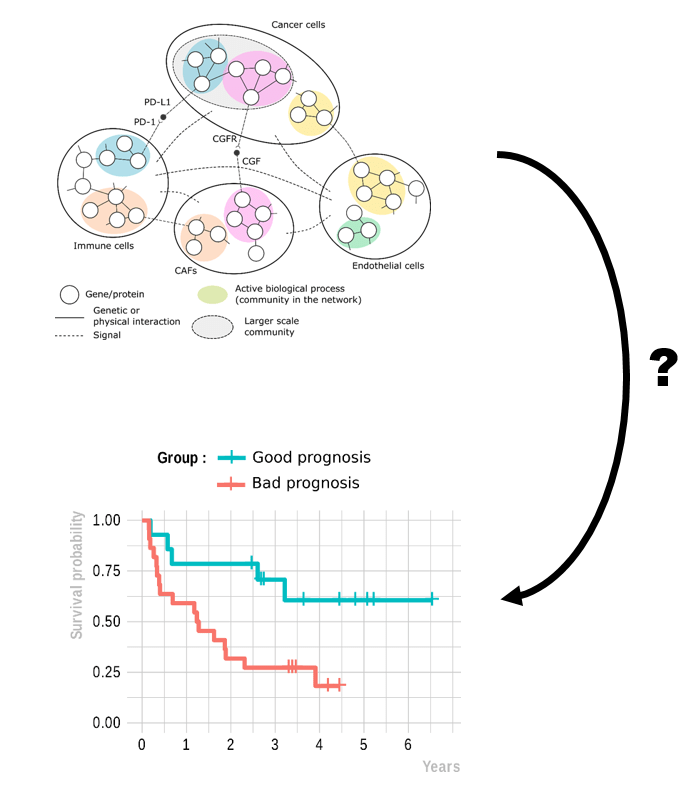
» Après 2 années de PACES j’ai intégré la licence Mathématiques et Informatique Appliquées aux Sciences Humaines et Sociales (MIASHS) en effectuant en parallèle une L2 Sciences de la vie à Montpellier. J’ai ensuite suivi le master de bioinformatique GENIOMHE à Paris Saclay avant de travailler un an à l’IGH en tant qu’ingénieur d’étude. J’ai finalement passé le concours CBS2 pour commencer une thèse en bioinformatique à l’IRCM portant sur la modélisation du microenvironnement tumoral par une approche d’intégration de données et de machine learning.
Je suis actuellement étudiant en doctorat à l’IRCM, travaillant sur la modélisation du microenvironnement tumoral grâce à l’intégration de données et de l’apprentissage automatique, au sein de l’équipe de Jacques Colinge. Je serai amené à développer des méthodes de Graph Neural Network (GNN) afin d’intégrer puis classifier des réseaux d’interactions inter et intra-cellulaires dans différents types de cancer.
« Je suis également membre de l’organisation du PhDPub, un événement mensuel de vulgarisation scientifique. Là-bas, des doctorants et des étudiants en master de toutes disciplines présentent leur sujet de recherche ou de stage en 10 minutes .Cet événement est une excellente occasion de partager nos connaissances avec un public plus large. »
Carla:
« Après avoir obtenu ma licence en biologie à l’UPVD, j’ai poursuivi mes études en me spécialisant dans la recherche en génétique humaine via le Master Génétique de l’UM. J’ai rapidement réalisé l’importance des compétences en informatique pour la recherche en biologie, ce qui m’a conduit à choisir le master en Bioinformatique de l’UM.
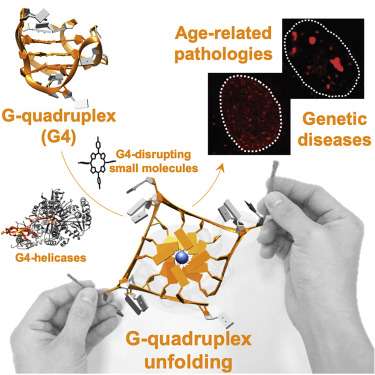
Mon sujet de thèse porte sur ‘Changing the paradigm of CpG islands by the integration of G4s as a novel definition factor,‘ ce qui exige des connaissances en génétique/épigénétique, des compétences de laboratoire, et surtout, des compétences en bioinformatique pour analyser mes propres données de séquençage. »
Nina:
Après avoir obtenu une licence en biotechnologies, je me suis réorientée pour étudier deux ans l’informatique en licence. J’ai ensuite lié ces deux domaines en entrant en master de bioinformatique. Mon stage de fin de master est allé de pair avec une thèse financée sur le même sujet, que j’ai commencé ce mois-ci. Ma thèse porte sur le transfert d’annotations dans des graphes de pangénome, qui est une structure de données qui vise à représenter toute la diversité génétique d’une espèce. Je vais devoir développer des méthodes et des outils pour intégrer des annotations de génome déjà existantes à des graphes de pangénome, ce qui permettra de mieux exploiter les informations contenues dans ces graphes. »
Marie :
J’ai réalisé mes deux premières années de licence en Biologie à l’université de Pau puis je me suis dirigée pour ma L3 vers la licence Biologie Ecologie à l’Université de Montpellier car je voulais travailler en Ecologie. J’ai finalement eu plus d’affinités pour la Biologie Evolutive et j’ai continué dans le Master Darwin (Master d’écologie et biologie évolutive) au cours duquel j’ai réalisé deux stages inscrits dans des thématiques d’évolution des génomes.
J’ai choisi de continuer en thèse avec mes encadrants de stage de M2, Nicolas Galtier et Nathanaëlle Saclier, sur un sujet différent, mais toujours inscrit dans la génomique évolutive et l’évolution moléculaire. J’ai pu avoir ma thèse en passant le concours de l’école doctorale GAIA dans la filière EERGP.
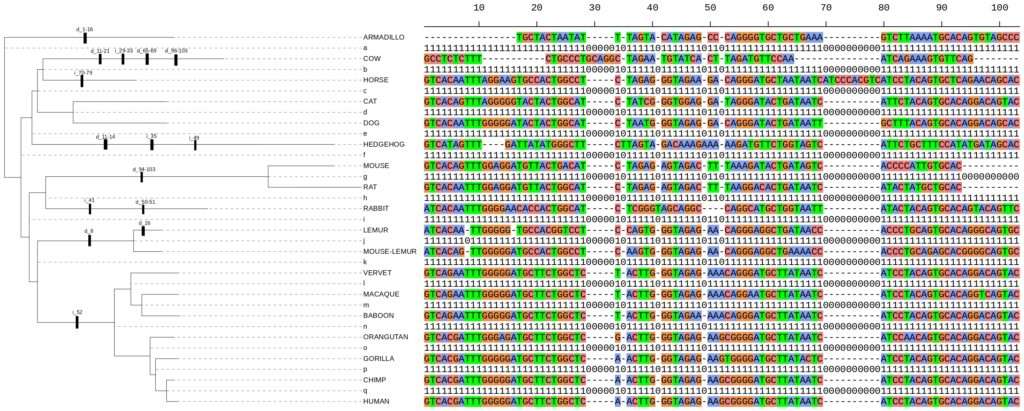
Ma thèse porte sur l’étude d’une force évolutive nommée la conversion génique biaisée (gBGC), qui est un biais de transmission associé à la recombinaison très répandu dans le monde vivant. C’est un processus qui peut favoriser la transmission de certains allèles indépendamment de leur valeur sélective et donc contrer la sélection naturelle et induire un fardeau génétique. Actuellement mon objectif est de caractériser le processus d’évolution compensatoire pouvant se produire pour restaurer la fonction des protéines après qu’elles aient été touchées par la gBGC. Pour cela j’utilise de l’analyse phylogénétique chez les rongeurs murinés et des outils bioinformatiques. Un second objectif sera de quantifier la force de la gBGC et le fardeau génétique qu’elle induit, grace à des modèles de génétique des populations, en utilisant comme modèle l’humain mais aussi d’autres groupes de Mammifères.
Jordan:
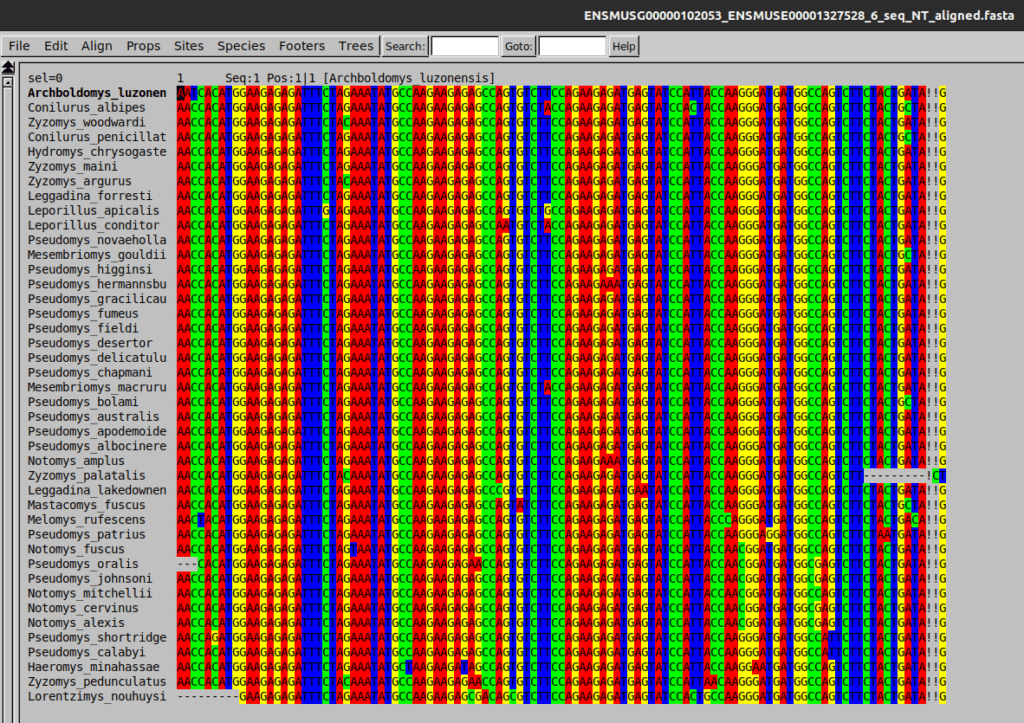
J’ai fait une licence de math option informatique, suivie d’une première année en master MIT (master en informatique théorique) puis une deuxième année en master ALGO après les changements de programme. J’ai fait mon stage de fin d’études au LIRMM dans l’équipe MAB, encadré par Fabio Pardi et Éric Rivals, sur l‘inférence des indels au cours de l’histoire évolutive de séquences biologiques. J’ai ensuite passé le concours de l’école doctorale I2S et réussi à obtenir une bourse de thèse pour continuer mon sujet de stage avec mes encadrants. Depuis, j’étudie la possibilité d’avoir un algorithme déterministe polynomial pour inférer le nombre minimal d’indels nécessaire à la justification des différences entre des séquences biologiques.